5.表型分析(TR-PhenoCluster)
说明
- 使用场景:泰立瑞开发的是QuPath系列插件的一个核心插件,专门用于高维细胞表型鉴定。其核心应用场景为:对多重免疫荧光(mIF)或成像质谱(CyTOF)等超多参数图像数据进行自动化的细胞分类和表型注释,为后续的空间分析提供精准的细胞身份信息。 1). 自动化细胞表型鉴定:解析包含少到2-10种、多达60+种蛋白标记物的复杂图像数据。支持监督或无监督的聚类算法,结合预训练的AI模型,自动识别并分类组织中的各种细胞类型,例如:免疫细胞亚群分析、识别不同状态的肿瘤细胞、基质细胞分析等, 2). 解决跨平台数据挑战:解决了不同平台(如PhenoCycler, Comet, Hyperion, CODEX等)数据的批次效应和鲁棒性问题 3). 作为空间分析流水线的上游模块:PhenoCluster通常与泰立瑞的另一款插件Spa协同工作,形成一个完整的分析链条:PhenoCluster负责“是什么”的问题,即精确地给每个细胞打上身份标签。Spa:负责“在哪里”和“和谁在一起”的问题
- 功能入口:菜单栏:Terrydr -> TR-PhenoCluster
- 测试数据:demo-wsi/GCexample.ome.tif
- 更详细的操作说明以及如何配置细胞分类请查看
操作步骤
- 导入测试图像到项目(桌面 -> demo-wsi -> GCexample.ome.tif)
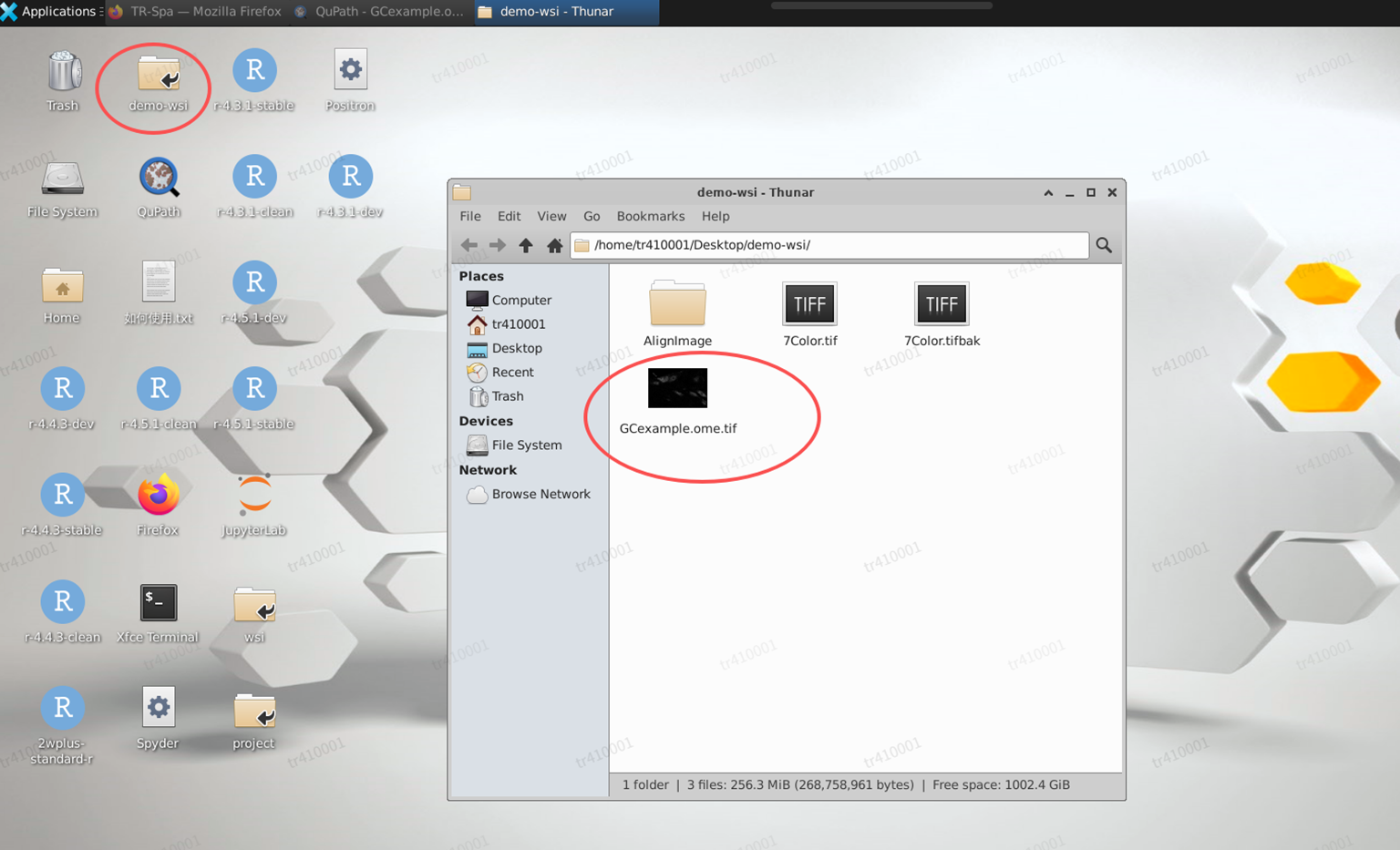
- 创建批注

细胞分割
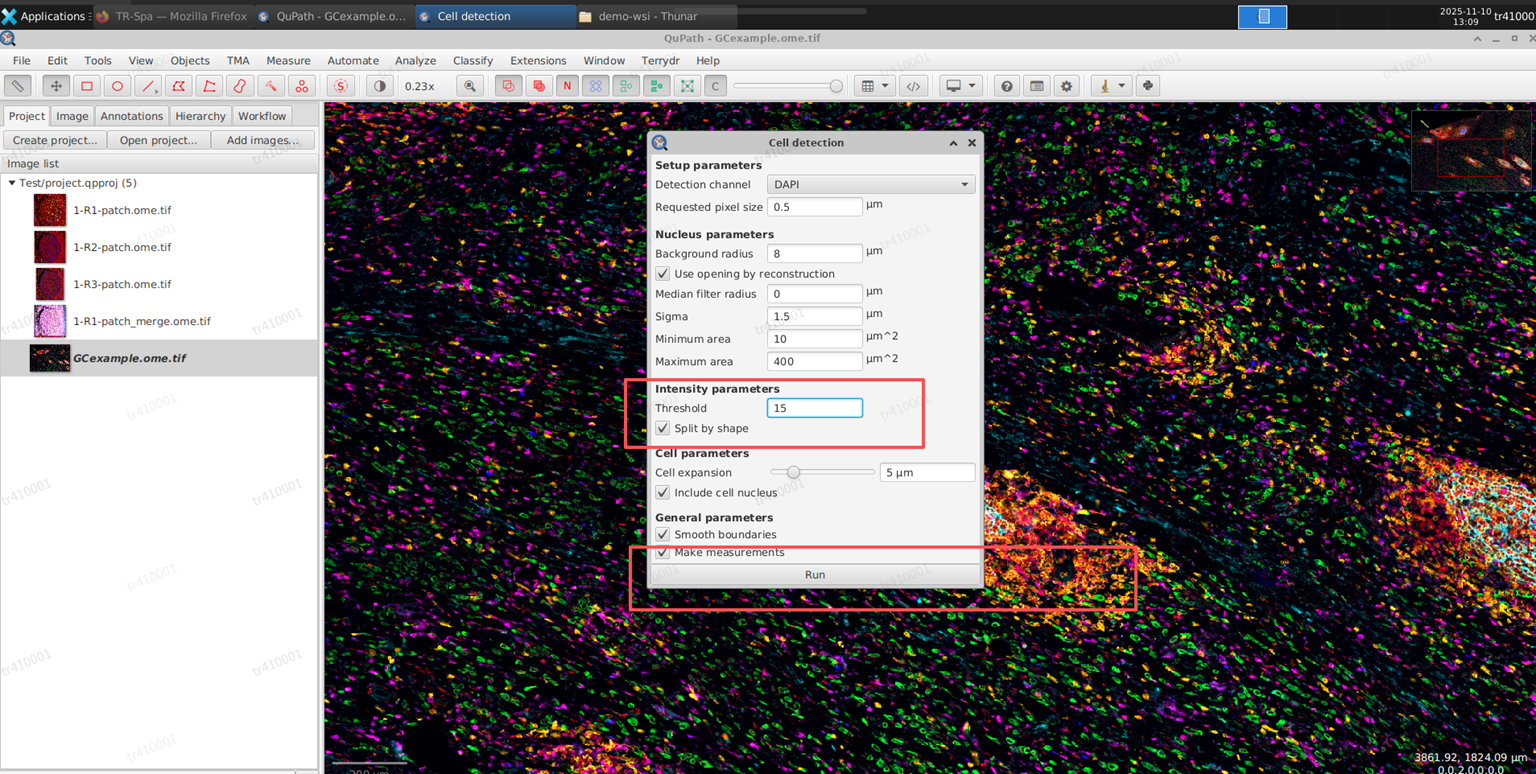
a. 使用QuPath自带的细胞分割 : 选中批注(双击批注,选中的为黄色边框) -> Analyze -> Cell detection -> Cell detection
b. 如果自带的细胞分割不准确, 可以使用TR-Seg分割, 可以查看本文档的 细胞分割(TR-Seg)
c. GCexample.ome.tif 这张图像的细胞分割的阈值参数可以填15, 点Run运行细胞分割

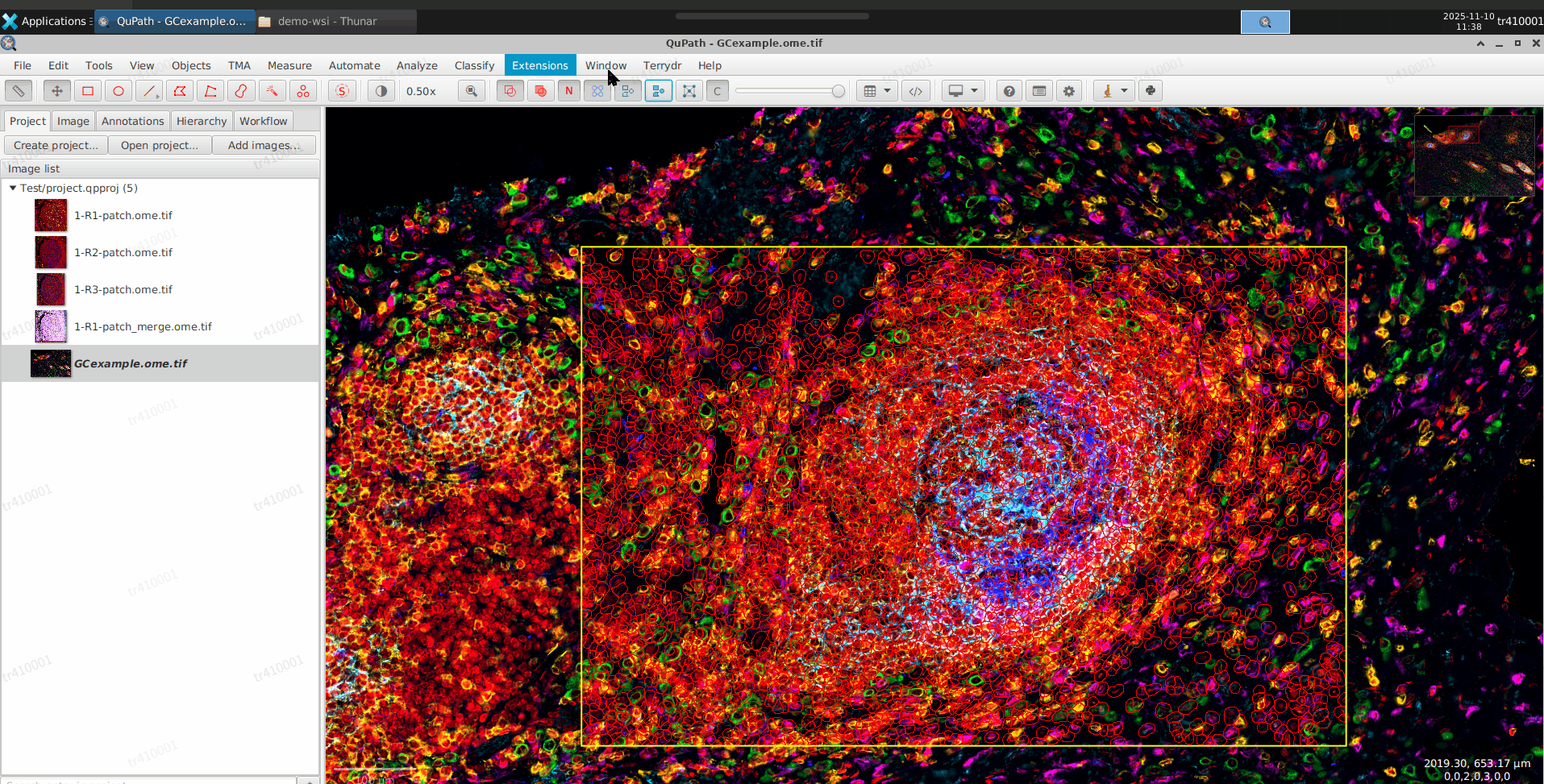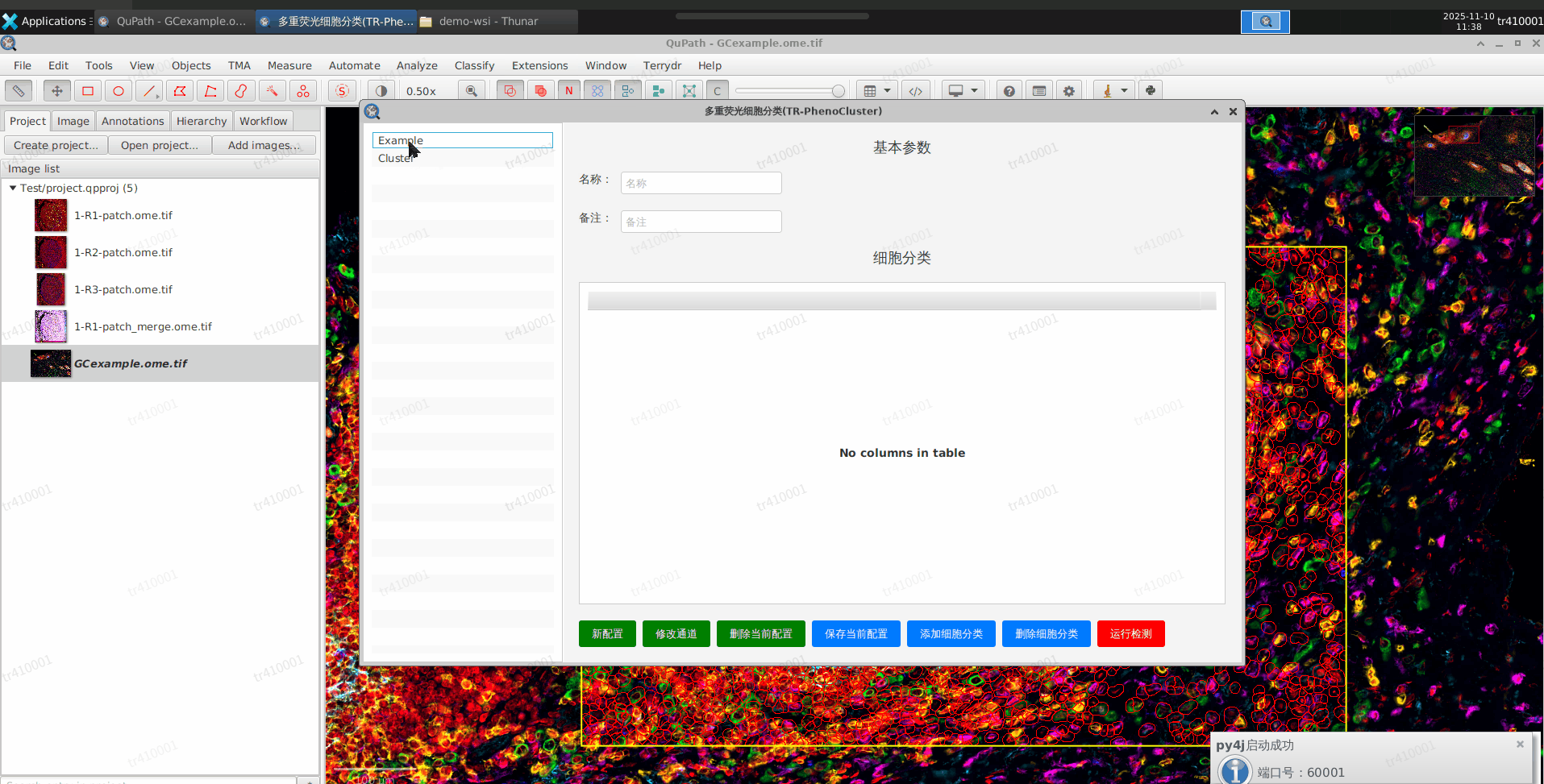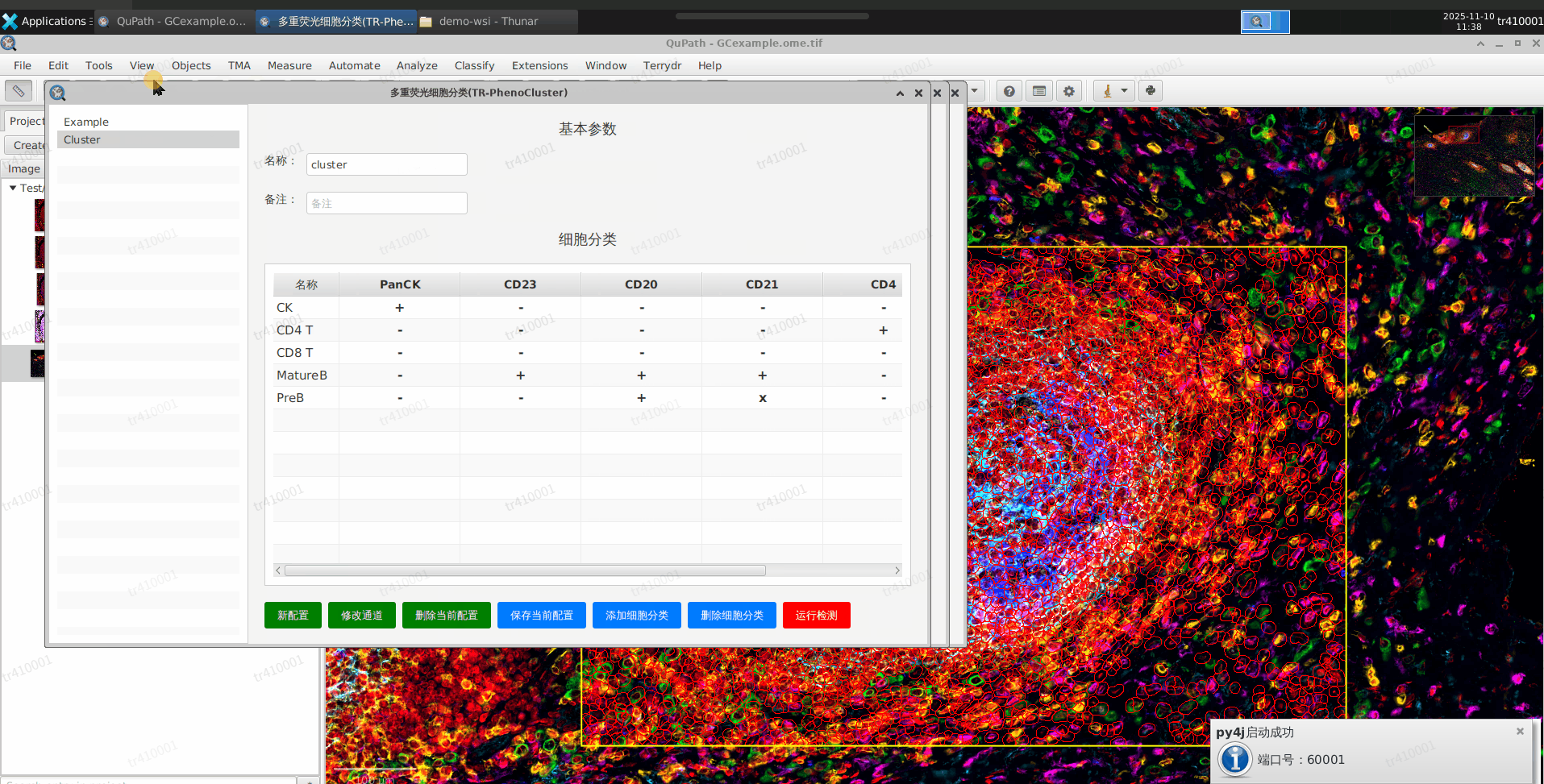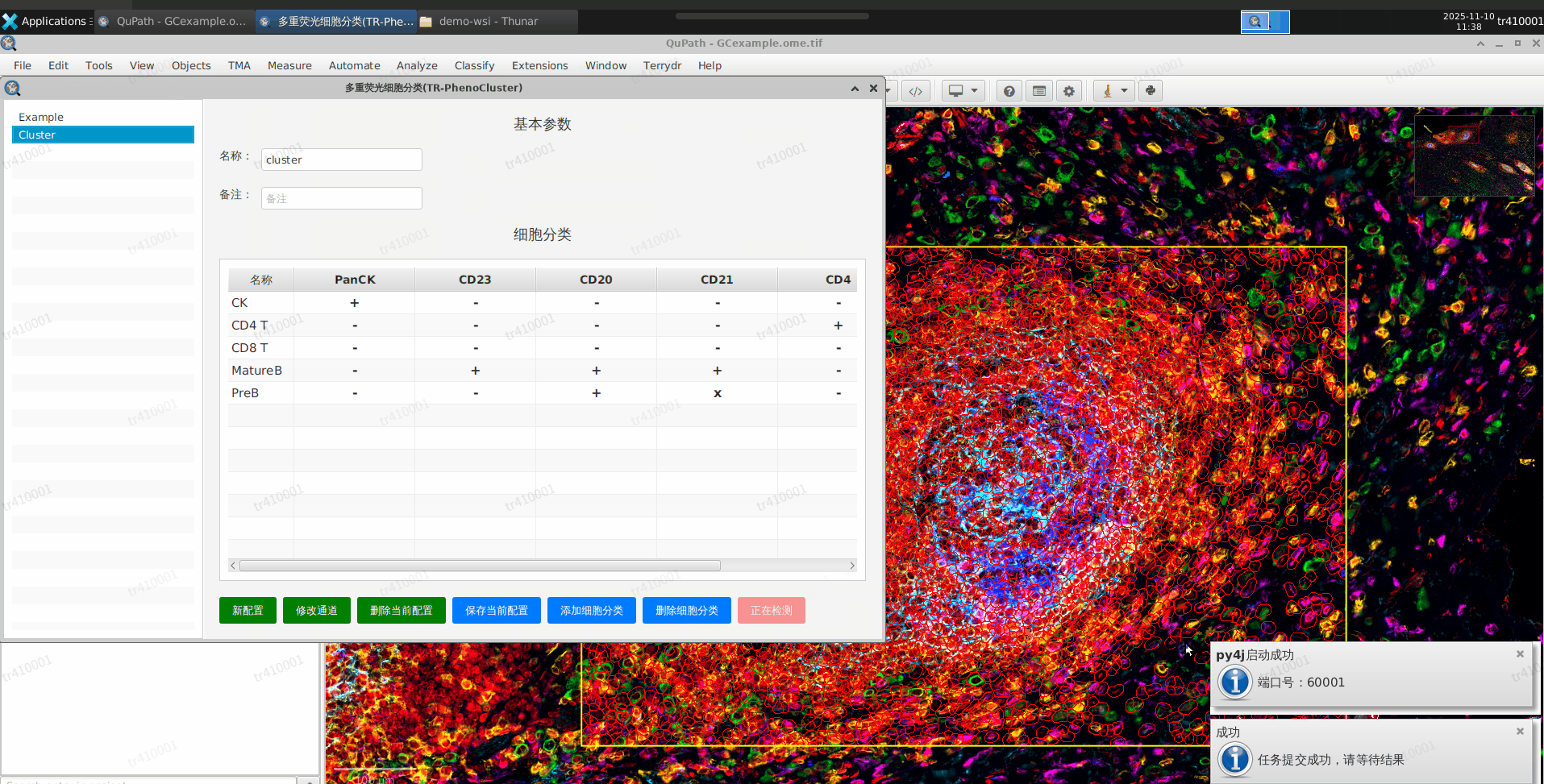
运行PhenoCluster
a. PhenoCluser是对细胞进行分类,所以需要在细胞分割之后运行
b. 打开Terrydr -> TR PhenoCluster
c. 选择配置,默认已创建一个Cluster的配置用于 GCexample.tif 图像
d. 可以直接选择Cluster,点击运行检测即可
检测结束,查看结果
a. 检测需要等待一些时间
b. 当检测结束后,系统会自动打开两个网页,分别是表型分析的结果和Spa空间分析

